Die
RNA-Interferenz
(kurz
RNAi
oder auch
RNA-Silencing
) ist ein naturlicher Mechanismus in den
Zellen
von Lebewesen mit einem
Zellkern
(
Eukaryoten
), welcher der zielgerichteten Abschaltung von
Genen
dient. Sie ist ein Spezialfall der
Gen-Stilllegung
. Die RNA-Interferenz beruht auf einer Wechselwirkung kurzer Stucke von
Ribonukleinsaure
(RNA) mit der
Erbinformation
-ubertragenden
mRNA
unter Beteiligung mehrerer
Enzymkomplexe
. Als Folge wird die mRNA in mehrere Bruchstucke gespalten und die zu ubertragende Information wird zerstort oder eine
Translation
in ein
Protein
verhindert.
In den Biowissenschaften hat sich RNA-Interferenz als eine neue Moglichkeit zur Stilllegung von
Genen
(?
Gen-Knockdown
“) etabliert. Seit 2018 sind bereits erste
RNAi-basierte Therapeutika
zugelassen, zahlreiche weitere werden
klinisch entwickelt
. Fur die Entdeckung des Mechanismus der RNA-Interferenz erhielten die beiden US-Wissenschaftler
Andrew Z. Fire
und
Craig C. Mello
2006 den
Nobelpreis fur Physiologie oder Medizin
.
 C. elegans
? ein Modellorganismus fur die Untersuchung der RNA-Interferenz
C. elegans
? ein Modellorganismus fur die Untersuchung der RNA-Interferenz
Das Phanomen der RNA-Interferenz kann in allen
Reichen
eukaryotischer
Lebewesen, einschließlich
Pilzen
,
Pflanzen
und
Tieren
, beobachtet werden. Daher wird angenommen, dass die RNA-Interferenz ein entwicklungsgeschichtlich sehr alter Mechanismus ist.
[1]
Besonders gut sind die Mechanismen der RNA-Interferenz in den biologischen
Modellorganismen
Arabidopsis thaliana
(Ackerschmalwand),
Caenorhabditis elegans
und
Drosophila melanogaster
untersucht. Insbesondere der
Fadenwurm
C. elegans
dient als Modellorganismus zur Erforschung der RNA-Interferenz, da in diesen relativ einfach gebauten Organismus besonders leicht interferierende RNA uber die als Nahrung dienenden genetisch veranderten
E.-coli
-Bakterien
eingebracht werden kann und bei ihm robuste Interferenzeffekte zu beobachten sind.
[2]
Einige Bestandteile der RNA-Interferenz-Maschinerie, wie beispielsweise die fur Funktion der RNA-Interferenz essenziellen
Argonautenproteine
, kommen auch in
Prokaryoten
vor.
[1]
Ein der RNA-Interferenz der Eukaryoten weitgehend ahnelnder Prozess ist der
CRISPR
-Mechanismus der Prokaryoten zur Verteidigung gegen das Eindringen fremden Erbguts durch
Viren
.
In der Natur kommen verschiedene Typen interferierender RNA vor. Wenngleich diese verschiedenen Typen interferierender RNA gemeinsame oder verwandte Mechanismen nutzen, so ist ihre Funktion zum Teil sehr verschiedenartig.
Die RNA-Interferenz spielt insbesondere bei Pflanzen bei der Verteidigung gegen fremde RNA eine wichtige Rolle. Sie stellt somit einen zentralen Bestandteil des pflanzlichen Abwehrsystems gegen
RNA-Viren
dar. An dieser Verteidigungsfunktion ist die
siRNA
(
small interfering RNA
), die in pflanzlichen Zellen als eine Folge der Infektion mit einem RNA-Virus bei der Vervielfaltigung (
Replikation
) der Virus-RNA gebildet wird und zugleich der Zelle zur Erkennung und Zerstorung dieser fremden RNA dient, beteiligt. Zahlreiche Viren versuchen ihrerseits uber eine Hemmung der an der RNA-Interferenz beteiligten Proteine, diesem Abwehrmechanismus zu entgehen.
[3]
Ahnliche Mechanismen der RNA-Interferenz zur Infektionsabwehr konnten auch bei Pilzen, Fadenwurmern und Insekten gefunden werden. Bei Saugetieren ist das Vorkommen eines korpereigenen siRNA-basierten Abwehrmechanismus nicht gesichert. Diese Aufgabe kann bei Saugetieren von spezieller zelleigener
miRNA
(
micro RNA
) mit einer direkten hemmenden Wirkung auf die Replikation von Viren wahrgenommen werden.
[3]
Die RNA-Interferenz spielt unter Beteiligung der zelleigenen miRNA bei vielen mehrzelligen Lebewesen bei der Regulation der
Genexpression
eine wichtige Rolle. Die im menschlichen Organismus auf etwa 1000 geschatzten verschiedenen miRNAs kontrollieren die Aktivitat von etwa 30 % der menschlichen Gene.
[4]
Hiervon sind unter anderem zahlreiche Funktionen des Immunsystems betroffen. Damit wird der Regulation der Genaktivitat durch miRNA eine ahnlich große Bedeutung beigemessen wie der Regulation durch
Transkriptionsfaktoren
.
Auch eine zelleigene Variante der siRNA, die sogenannte
esiRNA
(
endogenous siRNA
), ist an der Regulation der Genexpression beteiligt. Diese sowohl bei Pflanzen, Pilzen als auch Tieren vorkommende interferierende RNA dient im Gegensatz zur exogenen siRNA nicht der Virusabwehr.
[5]
Eine weitere Aufgabe, die Kontrolle sogenannter springender Gene (
Transposons
), wird insbesondere von einem weiteren Typ interferierender RNA-Molekule wahrgenommen, der piRNA (
PIWI interacting RNA
). Diese Funktion der RNA-Interferenz spielt beim Menschen eine besondere Rolle bei der
Spermatogenese
und der Entwicklung des
Embryos
.
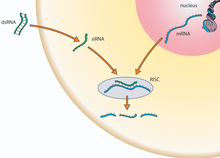 RNAi aktiviert einen Prozess, der zum Abbau von spezifischer mRNA fuhrt
RNAi aktiviert einen Prozess, der zum Abbau von spezifischer mRNA fuhrt
Es sind mehrere einander verwandte Mechanismen der RNA-Interferenz bekannt. An diesen Mechanismen sind als Komponenten kleine spezialisierte zumeist doppelstrangige RNA-Molekule, ein als
RNA-induced silencing complex
(RISC) bezeichneter Enzymkomplex und die Ziel-RNA beteiligt. Die RNA-Interferenz kann im Allgemeinen in drei Phasen unterteilt werden. Im ersten Schritt werden in der Zelle großere doppelstrangige RNA-Molekule mit Hilfe von
Ribonuklease
-Enzymen, wie
Dicer
und
Drosha
, in kurze doppelstrangige RNA-Fragmente geschnitten. Im zweiten Schritt werden diese Fragmente in Einzelstrange gespalten, und ein Strang, der sogenannte ?Leitstrang‘ (nicht zu verwechseln mit dem Leitstrang der
DNA-Replikation
), wird in den RISC-Enzymkomplex aufgenommen. Letztlich kann der aufgenommene Leitstrang den Enzymkomplex aktivieren, eine mRNA zu spalten, die in ihrer Basensequenz zu der Sequenz des Leitstrangs
komplementar
ist. Auf diese Weise bestimmt der Leitstrang, welche mRNA in welcher Weise gespalten wird. Alternativ dazu kann der Enzymkomplex die Funktion einer zum Leitstrang komplementaren mRNA als Informationsubertrager ohne Spaltung blockieren. Beide Wege konnen zu einer Unterdruckung der Umsetzung einer genetischen Information uber ein Protein in ein
Merkmal
fuhren.
[6]
 Strukturmodell von Dicer
Strukturmodell von Dicer
Ein erster zentraler Schritt der RNA-Interferenz ist die Bildung doppelstrangiger RNA-Molekule (dsRNA) mit einer Lange von etwa 20 bis 30
Basenpaaren
. Abhangig von ihrer Herkunft kann zwischen verschiedenen Typen kurzer doppelstrangiger RNA-Molekule unterschieden werden.
 siRNA
siRNA
Die siRNA, eine etwa 19 bis 23 Basenpaare umfassende doppelstrangige
kleine RNA
mit jeweils zwei 3'-endstandig uberstehenden
Nukleotiden
, wird durch eine Spaltung eines großen doppelstrangigen RNA-Molekuls gebildet. Diese Vorlaufer-RNA kann mehrere Hunderte bis Tausende Basenpaare lang sein und fallt beispielsweise bei der Vervielfaltigung viraler RNA an. dsRNA kann nicht nur exogenen, sondern auch endogenen Ursprungs sein.
[7]
An der Spaltung ist insbesondere das Enzym Dicer, eine sogenannte
RNase
III, beteiligt. Dieser Mechanismus wird insbesondere zur Verteidigung gegen RNA-Viren genutzt.
 Sekundarstruktur eines miRNA-Vorlaufers
Sekundarstruktur eines miRNA-Vorlaufers
Dem gegenuber ist die miRNA durch die
genomische
DNA
codiert. In einem mehrstufigen Prozess wird aus nichtproteincodierenden Bereichen der DNA die miRNA gebildet. Primar wird pri-miRNA (
primary miRNA
) mit Hilfe der
RNA-Polymerase II
durch
Transkription
als RNA-Einzelstrang erzeugt, der sich aufgrund betrachtlicher
palindromischer
Bereiche zu einer charakteristischen
Sekundarstruktur
faltet. In tierischen Zellen wird die pri-miRNA noch im
Zellkern
mit Hilfe eines Enzymkomplexes, dem
Microprocessor complex
, unter Beteiligung der RNase Drosha in die
haarnadelformige
pre-miRNA (
precursor miRNA
) mit einer Lange von 65 bis 70 Nukleotiden gespalten. Die gebildete pre-miRNA wird schließlich im
Zytosol
mit Hilfe von Dicer in einen jeweils etwa 21 bis 25 Basenpaare umfassenden miRNA-Doppelstrang geschnitten. In pflanzlichen Zellen hingegen erfolgt die Bildung eines miRNA-Doppelstrangs direkt aus der pri-miRNA unter Beteiligung der im Zellkern lokalisierten RNase
DCL1
.
Eine in tierischen
Geschlechtszellen
vorkommende Variante der RNA-Interferenz nutzt einzelstrangige piRNA (
PIWI
-interacting RNA). Die Bildung dieser etwa 24 bis 31 Nukleotide umfassenden interferierenden RNA-Molekule unterscheidet sich wesentlich von der der siRNA und miRNA. An der noch nicht vollstandig aufgeklarten Biogenese der piRNA sind weder doppelstrangige RNA-Vorlaufermolekule noch RNAsen vom Typ III beteiligt. Es wird unter anderem angenommen, dass die piRNA nach der Bildung eines Primartranskripts durch Transkription eines piRNA-Clusters in einem als Ping-Pong-Mechanismus bezeichneten Kreislaufprozess unter Beteiligung von
PIWI-Proteinen
gebildet wird.
[8]
Neben diesen interferierenden RNAs sind weitere zur RNA-Interferenz befahigte RNA-Typen, wie beispielsweise
21U-RNA
[9]
und die esiRNA
[5]
, bekannt.
 Oberflachenstrukturmodell eines Argonautenproteins (grau) mit gebundenen Leit- (rot) und Zielstrang (grun)
Oberflachenstrukturmodell eines Argonautenproteins (grau) mit gebundenen Leit- (rot) und Zielstrang (grun)
Das zentrale Glied der RNA-Interferenz ist ein als
RNA-induced silencing complex
(RISC) bezeichneter Enzymkomplex. Die von Dicer gebildeten doppelstrangigen siRNA- oder miRNA-Molekule werden an die
Argonautenproteine
des
RNA-induced silencing complex
ubergeben. Dieser mit doppelstrangiger RNA beladene Komplex wird auch als Pra-RISC bezeichnet. Es werden innerhalb des Pra-RISC die Doppelstrange der gebundenen siRNA oder miRNA gespalten. Der als Leitstrang bezeichnete RNA-Einzelstrang verbleibt im
RNA-induced silencing complex
, der in diesem Zustand Holo-RISC genannt wird, wahrend der andere Strang den Komplex verlasst und abgebaut wird. Schließlich wird eine zum Leitstrang komplementare mRNA in den
RNA-induced silencing complex
eingebaut.
Die am besten erforschte Konsequenz aus der Aktivierung des
RNA-induced silencing complex
ist die Spaltung einer im Komplex gebundenen und zum Leitstrang komplementaren mRNA. Dieser Mechanismus, der insbesondere bei siRNA beobachtet werden kann, setzt ein Argonautenprotein mit
Endonuklease
-Aktivitat und eine moglichst perfekte Komplementaritat zwischen Leitstrang und Ziel-mRNA voraus.
[10]
Von den vier Argonautenproteinen des Menschen, die an der siRNA- oder miRNA-vermittelten RNA-Interferenz beteiligt sind, besitzt lediglich AGO2 eine Endonukleaseaktivitat.
[11]
Eine Spaltung der Ziel-RNA kann daruber hinaus als eine Folge der piRNA-vermittelten RNA-Interferenz beobachtet werden. Diese Spaltung ist auf die Endonukleaseaktivitat der im Ping-Pong-Zyklus beteiligten PIWI-Proteine zuruckzufuhren. Die gespaltene Ziel-mRNA kann in den P-Bodys weiter abgebaut werden.
Die wichtigste Funktion des
RNA-induced silencing complex
(insbesondere bei der miRNA-vermittelten RNA-Interferenz) ist die Hemmung der Ubersetzung der Information einer mRNA in ein Protein an den
Ribosomen
(Translation). Fur diese Funktion ist weder eine Endonukleaseaktivitat noch eine hochgradige Komplementaritat zwischen dem Leitstrang und der Ziel-mRNA Voraussetzung. Lediglich die Nukleotide 2 bis 7 des Leitstrangs mussen zu denen der Ziel-mRNA komplementar sein.
[12]
Die zugrundeliegenden molekularen Mechanismen der Translationshemmung sind weniger gut erforscht. Mindestens zwei mogliche Mechanismen, die in den Zellen der Taufliege
Drosophila melanogaster
bereits beobachtet werden konnten, werden fur die Hemmung der Umsetzung der mRNA-Information in ein Protein verantwortlich gemacht. Zum einen kann der
RNA-induced silencing complex
uber
Protein-Protein-Wechselwirkungen
mit
Translationsinitialisierungsfaktoren
blockieren. Zum anderen kann ein Abbau des
Polyadenylierungssignals
der mRNA durch den aktivierten
RNA-induced silencing complex
beobachtet werden. Beide Mechanismen haben eine Hemmung der Translation zur Folge.
[13]
Neben der RNA-Interferenz konnen kleine doppelstrangige RNA-Molekule zu einer Hemmung der Transkription fuhren. An diesem im Zellkern stattfindenden sogenannten
transkriptionellen Gen-Silencing
ist eine als
RNA-induced transcriptional silencing complex
(RITS) bezeichnete Variante des
RNA-induced silencing complex
beteiligt. Der aktivierte
RNA-induced transcriptional silencing complex
fuhrt uber
Histonmodifikationen
zur Bildung von
Heterochromatin
-Bereichen des Erbguts. Diese Bereiche sind nicht mehr fur die Enzyme der Transkription zuganglich.
Ein weiteres, auf kleine RNA-Molekule zuruckzufuhrendes Phanomen neben der RNA-Interferenz ist die sogenannte
RNA-Aktivierung
(RNAa). Als zugrundeliegende Mechanismen werden eine Aktivierung der Transkription durch
Promotor
-spezifische interferierende RNA, eine Aktivierung der Translation unter Beteiligung von Argonautenproteinen, eine Wechselwirkung mit zelleigener miRNA und
Antisense
-Mechanismen diskutiert.
[14]
[15]
[16]
 Prinzip der Anwendung des RNA-Interferenz zur Ausschaltung eines Gens mit Hilfe von
Lentiviren
Prinzip der Anwendung des RNA-Interferenz zur Ausschaltung eines Gens mit Hilfe von
Lentiviren
Die RNA-Interferenz wird in der
Grundlagenforschung
zur Aufklarung der noch unbekannten Funktion eines zu untersuchenden bekannten Gens und dessen codierten Proteins genutzt. Die RNA-Interferenz erlaubt die gezielte Ausschaltung jedes beliebigen Gens. Aus dieser Ausschaltung kann die Funktion des von Gen codierten Proteins abgeleitet werden. Es muss einzig die Nukleotidsequenz des zu untersuchenden Gens bekannt sein, um potenziell interferierende RNA-Molekule zu entwickeln. Damit ist die auch als ?Gen-Knockdown“ bezeichnete Anwendung der RNA-Interferenz zur Untersuchung der Funktion eines Gens und dessen codierten Proteins deutlich weniger aufwendig als das konventionelle
Gen-Knockout
. Zudem ist die Anwendung der RNA-Interferenz zeit- und erfolgversprechender als die Entwicklung eines
Liganden
als
Inhibitor
der Proteinfunktion. Dies ist insbesondere der Fall, wenn eine pharmakologische Unterscheidung nahe verwandter Proteine praktisch unmoglich ist.
[4]
Auch fur die umgekehrte Fragestellung, die Suche nach den fur eine bekannte Funktion oder ein bestimmtes Merkmal verantwortlichen Genen oder Proteinen, eignet sich die experimentelle Nutzung der RNA-Interferenz. Hierfur werden RNA-Interferenzbibliotheken mit interferierenden RNAs gegen jedes einzelne Gen eingesetzt, die mit Hilfe des
Hochdurchsatz-Screenings
genutzt werden. Diese sogenannten genomweiten RNA-Interferenzscreenings finden auch in der
Pharmaforschung
auf der Suche nach neuen Zielmolekulen fur neue Wirkstoffe (
Target discovery
) Anwendung.
Fur beide Anwendungsgebiete der RNA-Interferenz in der Grundlagenforschung werden insbesondere synthetische siRNA- oder
shRNA
-Molekule (
short hairpin RNA
) eingesetzt. Sie werden entweder direkt mit Hilfe diverser
Transfektionstechniken
in die Zellen eingeschleust oder indirekt in den Zellen nach Einbringung eines
Vektors
, wie beispielsweise eines shRNA-codierenden
Plasmids
oder eines
Virus
, unter Ausnutzung der zellularen Transkription gebildet. Zur Vermeidung einer Fehlinterpretation durch die in der Praxis immer wieder auftretenden unspezifischen Effekte werden geeignete Kontrollexperimente durchgefuhrt oder die Spezifitat wird mit Hilfe mehrerer interferierender RNAs gegen ein und dasselbe Gen bestatigt.
[4]
 Bevasiranib
Bevasiranib
Obgleich die RNA-Interferenz ein erst kurzlich entdeckter biologischer Mechanismus ist, sind die ersten RNA-Interferenz-basierten Therapeutika bereits in den USA und auch der EU zugelassen. 2018 wurde mit
Patisiran
das erste RNAi-basierte Medikament zugelassen.
[17]
[18]
Patisiran zielt auf die TTR-mRNA mit dem Ziel einer Reduktion des Proteins TTR, das in der Leber gebildet wird. Bei Patienten mit
hereditarer
Transthyrethin-Amyloidose (hATTR)
liegt eine Mutation im TTR-Gen vor. Infolgedessen werden fehlerhafte TTR-Proteine gebildet, die sich nicht korrekt in einer Tetramer-Struktur falten. Durch die fehlerhafte Faltung verklumpen die TTR-Proteine und lagern sich in Organen und Gewebe ab (
Amyloid
), was zu Funktionsstorungen im Organismus fuhrt. Durch das Herunterfahren der TTR-Produktion kann die Progression der Erkrankung gestoppt werden.
2019 und 2020 folgten mit den Zulassungen von
Givosiran
zur Behandlung der
Akuten intermittierenden Porphyrie
[19]
[20]
und
Lumasiran
zur Behandlung der
Primaren Hyperoxalurie Typ 1
[21]
[22]
die nachsten RNAi-Therapeutika zur Behandlung seltener, genetisch bedingter Erkrankungen. Mit
Inclisiran
wurde Ende 2020 zudem erstmals ein siRNA-basierter Wirkstoff zur Behandlung der
familiaren Hypercholesterinamie
zugelassen. Am weitesten fortgeschritten in der Entwicklung von RNAi-basierten Therapeutika gilt das Unternehmen
Alnylam Pharmaceuticals
aus den USA. Alle bislang zugelassenen RNAi-Therapeutika stammen aus der Entwicklung von Alnylam. Inclisiran wurde auslizensiert an
The Medicines Company
, die 2020 von
Novartis
gekauft wurden.
Diese rasante Entwicklung kann zum einen auf das Potenzial der RNA-Interferenz als therapeutische Methode und andererseits auf die jahrelange Erfahrung mit
Antisense-Oligonukleotiden
und
Ribozymen
in der klinischen Entwicklung zuruckgefuhrt werden.
[4]
Am weitesten fortgeschritten war die Entwicklung von
Bevasiranib
, einer gegen den
Vascular Endothelial Growth Factor
(VEGF) gerichteten siRNA, die zur Behandlung der altersbedingten
Makuladegeneration
eingesetzt werden sollte, jedoch in einer klinischen Studie der Phase III scheiterte. Kurz nach diesem Ruckschlag stellten mehrere große
pharmazeutische Unternehmen
, darunter
Hoffmann-La Roche
, ihre auf siRNA basierenden Entwicklungsprogramme ein.
[23]
Ungeachtet dessen befinden sich weitere RNA-Interferenz-basierte Therapeutika, wie die gegen den
VEGF-Rezeptor
-1 gerichtete
Sirna-027
und die gegen das Gen
RTP801
gerichtete
PF-655
zur Behandlung der altersbedingten Makuladegeneration sowie die gegen ein virales
Nukleokapsid
gerichtete
ALN-RSV01
zur Behandlung von
Respiratory-Syncytial-Virus
-Infektionen, derzeit mindestens in Phase II der klinischen Erprobung.
[24]
Auch zelleigene interferierende RNAs stellen potenzielle Ziele fur die pharmazeutische Entwicklung dar. Sogenannte
Antagomire
, welche zelleigene miRNAs uber Antisense-Mechanismen blockieren, befinden sich in der praklinischen Entwicklung.
[25]
 Genausschaltung durch RNA-Ubertragung wurde in Petunien entdeckt (links:
Wildtyp
, Mitte und rechts: nach RNA-Interferenz)
Genausschaltung durch RNA-Ubertragung wurde in Petunien entdeckt (links:
Wildtyp
, Mitte und rechts: nach RNA-Interferenz)
Um das Jahr 1990 versuchte die Forschergruppe um
Joseph Mol
und
Richard Jorgensen
, die Blutenfarbung von
Petunien
zu verstarken.
[26]
Sie beabsichtigten, zusatzliche Kopien des Gens
Dihydroflavonolreduktase
in die Pflanzen einzubringen, und hofften dadurch die Produktion der Blutenfarbstoffe (aus der Gruppe der
Flavonoide
) anregen zu konnen. Das Gegenteil war jedoch der Fall. Zur Uberraschung aller waren die meisten der genetisch veranderten Pflanzen weniger stark gefarbt als unbehandelte Pflanzen, einige sogar schneeweiß. Fur dieses Phanomen wurde zunachst der Begriff ?Cosuppression“ gepragt, da nicht nur die in die Pflanzen eingebrachten Gene, sondern auch das korrespondierende, naturlich in den Pflanzen vorkommende Gen der Dihydroflavonolreduktase kein bzw. nur wenig funktionelles Protein lieferte.
Weitere Arbeiten zeigten einige Jahre spater, dass die Gene nicht nur auf der Ebene der Transkription abgeschaltet wurden, sondern dass zusatzlich die von ihnen produzierte mRNA in den Zellen schnell abgebaut wurde ? ein Vorgang, der
Post-Transcriptional Gene Silencing
(PTGS) getauft wurde. Etwa zur gleichen Zeit wurden ahnliche Phanomene aus Pilzen (
Neurospora crassa
) unter dem Namen
Quelling
, aus
Algen
und aus dem Fadenwurm
C. elegans
beschrieben.
 Andrew Z. Fire
Andrew Z. Fire
1998 schließlich war nach einer Reihe von Untersuchungen klar, dass die
mRNA
selbst maßgeblich an dem Phanomen des PTGS beteiligt ist. Fast gleichzeitig mit der vollstandigen
Sequenzierung
des
Genoms
von
C. elegans
beschrieben Andrew Fire und Craig Mello 1998 die Technik der RNA-Interferenz (RNAi), bei der doppelstrangige RNA in
C. elegans
zu einem effizienten und spezifischen Gen-Knockdown fuhrt.
[27]
Hierfur wurde ihnen der
Nobelpreis
fur Physiologie oder Medizin des Jahres 2006 zuerkannt. Wie genau das Einbringen von doppelstrangiger RNA in den Organismus jedoch zum Abbau der Ziel-RNA fuhrt, wurde erst klar, als 1999
Andrew J. Hamilton
und
David C. Baulcombe
kurze RNA-Molekule mit einer Lange von etwa 25 Nukleotiden isolieren konnten, die in direktem Zusammenhang zu der regulierten RNA steht: die siRNA, die der RNAi ihre Spezifitat verleiht, indem sie die Ziel-RNA uber Basenpaarung binden.
[28]
Bei dem Versuch, die von Craig Mello und Andrew Fire verwendete Strategie auf
Wirbeltiere
zu ubertragen, traten jedoch in der Folgezeit erhebliche Probleme auf: Die verwendeten Zellen schienen die langen doppelstrangigen RNAs nicht zu tolerieren, und es kam zum programmierten Zelltod (
Apoptose
). Erst 2001 veroffentlichten
Sayda Elbashir
und
Thomas Tuschl
einen Weg, wie dieses Problem umgangen werden kann. Sie verwendeten kurze doppelstrangige RNA mit je 21 Nukleotiden, die nicht zu einer Apoptose fuhren, aber funktionell fur ein Gen-Silencing ausreichend sind.
[29]
Es wurde postuliert, dass interferierende RNA bei der Abwehr von RNA-Viren und bei der Regulation einiger mobiler genetischer Elemente (Transposone) eine Rolle spielen konnten. Daher versuchte man ? motiviert durch die Tatsache, dass die RNA-Interferenz einen in Eukaryoten wohl universellen Prozess darstellt ? interferierende RNA aus unbehandelten Zellen zu isolieren. So stieß man auf eine weitere Gruppe von kleinen RNA-Molekulen, die
miRNAs
. Zwei dieser miRNAs,
lin-4
und
let-7
, waren bereits zuvor in
C. elegans
entdeckt und zunachst als stRNAs (
small temporal RNAs
) bezeichnet worden.
- Jochen Graw:
Genetik
. Springer, Berlin; 5., vollstandig uberarbeitete Auflage 2010;
ISBN 978-3-642-04998-9
; S. 313ff.
- Jocelyn E. Krebs, Elliott S. Goldstein und Stephen T. Kilpatrick:
Lewin's Genes X
. Jones & Bartlett Pub (Ma); 10. Auflage 2010;
ISBN 978-0-7637-6632-0
; S. 861ff.
- Siomi H, Siomi MC:
On the road to reading the RNA-interference code
. In:
Nature
. 457. Jahrgang,
Nr.
7228
, Januar 2009,
S.
396?404
,
doi
:
10.1038/nature07754
,
PMID 19158785
.
- Jinek M
,
Doudna JA
:
A three-dimensional view of the molecular machinery of RNA interference
. In:
Nature
. 457. Jahrgang,
Nr.
7228
, Januar 2009,
S.
405?412
,
doi
:
10.1038/nature07755
,
PMID 19158786
.
- ↑
a
b
Cerutti H, Casas-Mollano JA:
On the origin and functions of RNA-mediated silencing: from protists to man
. In:
Curr. Genet.
50. Jahrgang,
Nr.
2
, August 2006,
S.
81?99
,
doi
:
10.1007/s00294-006-0078-x
,
PMID 16691418
,
PMC 2583075
(freier Volltext).
- ↑
Kamath RS, Ahringer J:
Genome-wide RNAi screening in Caenorhabditis elegans
. In:
Methods
. 30. Jahrgang,
Nr.
4
, August 2003,
S.
313?321
,
PMID 12828945
.
- ↑
a
b
Haasnoot J, Westerhout EM, Berkhout B:
RNA interference against viruses: strike and counterstrike
. In:
Nat. Biotechnol.
25. Jahrgang,
Nr.
12
, Dezember 2007,
S.
1435?1443
,
doi
:
10.1038/nbt1369
,
PMID 18066040
.
- ↑
a
b
c
d
Kurreck J:
RNA interference: from basic research to therapeutic applications
. In:
Angew. Chem. Int. Ed. Engl.
48. Jahrgang,
Nr.
8
, 2009,
S.
1378?1398
,
doi
:
10.1002/anie.200802092
,
PMID 19153977
.
- ↑
a
b
Sontheimer EJ, Carthew RW:
Silence from within: endogenous siRNAs and miRNAs
. In:
Cell
. 122. Jahrgang,
Nr.
1
, Juli 2005,
S.
9?12
,
doi
:
10.1016/j.cell.2005.06.030
,
PMID 16009127
.
- ↑
Siomi H, Siomi MC:
On the road to reading the RNA-interference code
. In:
Nature
. 457. Jahrgang,
Nr.
7228
, Januar 2009,
S.
396?404
,
doi
:
10.1038/nature07754
,
PMID 19158785
.
- ↑
Jochen Graw:
Genetik
. Springer, Berlin; 5., vollstandig uberarbeitete Auflage 2010;
ISBN 978-3-642-04998-9
; S. 317.
- ↑
Aravin AA, Hannon GJ, Brennecke J:
The Piwi-piRNA pathway provides an adaptive defense in the transposon arms race
. In:
Science
. 318. Jahrgang,
Nr.
5851
, November 2007,
S.
761?764
,
doi
:
10.1126/science.1146484
,
PMID 17975059
.
- ↑
Ruby JG, Jan C, Player C,
et al.
:
Large-scale sequencing reveals 21U-RNAs and additional microRNAs and endogenous siRNAs in C. elegans
. In:
Cell
. 127. Jahrgang,
Nr.
6
, Dezember 2006,
S.
1193?1207
,
doi
:
10.1016/j.cell.2006.10.040
,
PMID 17174894
.
- ↑
Liu J, Carmell MA, Rivas FV,
et al.
:
Argonaute2 is the catalytic engine of mammalian RNAi
. In:
Science
. 305. Jahrgang,
Nr.
5689
, September 2004,
S.
1437?1441
,
doi
:
10.1126/science.1102513
,
PMID 15284456
.
- ↑
Pratt AJ, MacRae IJ:
The RNA-induced silencing complex: a versatile gene-silencing machine
. In:
J. Biol. Chem.
284. Jahrgang,
Nr.
27
, Juli 2009,
S.
17897?178901
,
doi
:
10.1074/jbc.R900012200
,
PMID 19342379
,
PMC 2709356
(freier Volltext).
- ↑
Lewis BP, Burge CB, Bartel DP:
Conserved seed pairing, often flanked by adenosines, indicates that thousands of human genes are microRNA targets
. In:
Cell
. 120. Jahrgang,
Nr.
1
, Januar 2005,
S.
15?20
,
doi
:
10.1016/j.cell.2004.12.035
,
PMID 15652477
.
- ↑
Iwasaki S, Kawamata T, Tomari Y:
Drosophila argonaute1 and argonaute2 employ distinct mechanisms for translational repression
. In:
Mol. Cell
. 34. Jahrgang,
Nr.
1
, April 2009,
S.
58?67
,
doi
:
10.1016/j.molcel.2009.02.010
,
PMID 19268617
.
- ↑
Li LC, Okino ST, Zhao H,
et al.
:
Small dsRNAs induce transcriptional activation in human cells
. In:
Proc. Natl. Acad. Sci. U.S.A.
103. Jahrgang,
Nr.
46
, November 2006,
S.
17337?42
,
doi
:
10.1073/pnas.0607015103
,
PMID 17085592
,
PMC 1859931
(freier Volltext).
- ↑
Vasudevan S, Tong Y,
Steitz JA
:
Switching from repression to activation: microRNAs can up-regulate translation
. In:
Science
. 318. Jahrgang,
Nr.
5858
, Dezember 2007,
S.
1931?4
,
doi
:
10.1126/science.1149460
,
PMID 18048652
.
- ↑
Krutzfeldt J, Rajewsky N, Braich R,
et al.
:
Silencing of microRNAs in vivo with 'antagomirs'
. In:
Nature
. 438. Jahrgang,
Nr.
7068
, Dezember 2005,
S.
685?689
,
doi
:
10.1038/nature04303
.
- ↑
FDA approves first-of-its kind targeted RNA-based therapy to treat a rare disease
, PM FDA vom 10. August 2018, abgerufen am 30. Marz 2021
- ↑
EMA:
Onpattro.
European Medicines Agency,
abgerufen am 30. Marz 2021
(englisch).
- ↑
FDA approves first treatment for inherited rare disease.
In:
FDA.
20. November 2019,
abgerufen am 30. Marz 2021
.
- ↑
K. Graefe:
Erstes Medikament fur seltene Erbkrankheit
,
Pharmazeutische Zeitung
, vom 10. Marz 2020, abgerufen am 30. Marz 2021
- ↑
FDA Approves First Drug to Treat Rare Metabolic Disorder
, PM FDA vom 23. November 2020, abgerufen am 31. Marz 2021
- ↑
Oxlumo
, Website der EMA, abgerufen am 31. Marz 2021
- ↑
Ledford H:
Drug giants turn their backs on RNA interference
. In:
Nature
. 468. Jahrgang,
Nr.
7323
, November 2010,
S.
487
,
doi
:
10.1038/468487a
,
PMID 21107398
.
- ↑
Tiemann K, Rossi JJ:
RNAi-based therapeutics-current status, challenges and prospects
. In:
EMBO Mol Med
. 1. Jahrgang,
Nr.
3
, Juni 2009,
S.
142?151
,
doi
:
10.1002/emmm.200900023
,
PMID 20049714
.
- ↑
Alderton GK:
Therapy: A big step for targeting RNAs
. In:
Nature Reviews Cancer
. 10. Jahrgang, 2010,
S.
313
,
doi
:
10.1038/nrc2848
.
- ↑
Napoli C, Lemieux C, Jorgensen R:
Introduction of a chalcone synthase gene into Petunia results in reversible co-suppression of homologous genes in trans
. In:
Plant Cell
. 2. Jahrgang,
Nr.
4
, 1990,
S.
279?289
,
PMID 12354959
,
PMC 159885
(freier Volltext).
- ↑
Fire A., Xu S., Montgomery M.K., Kostas S.A., Driver S.E., Mello C.C.:
Potent and specific genetic interference by double-stranded RNA in Caenorhabditis elegans
. In:
Nature
. 391. Jahrgang, 1998,
S.
806?811
,
PMID 9486653
(
nature.com
[PDF]).
- ↑
Hamilton A.J., Baulcombe D.C.:
A species of small antisense RNA in posttranscriptional gene silencing in plants
. In:
Science
. 286. Jahrgang,
Nr.
5441
, 1999,
S.
950?952
,
PMID 10542148
.
- ↑
Elbashir S.M., Harborth J., Lendeckel W., Yalcin A., Weber K., Tuschl T.:
Duplexes of 21-nucleotide RNAs mediate RNA interference in cultured mammalian cells
. In:
Nature
. 411. Jahrgang, 2001,
S.
494?498
,
PMID 11373684
.